Shixiang Wang (王诗翔)
Shixiang Wang (王诗翔)
``` library(UCSCXenaShiny) library(dplyr) library(purrr) library(tidyr) geneList = c("TP53", "KRAS", "PTEN", "ERBB2", "MYC") alldata = purrr::map(geneList, query_pancan_value) expr = purrr::reduce( purrr::map2(alldata, geneList, function(.x, .y) { dt = data.frame(sample = names(.x$expression), expr...
#245 代码可以复用
目前 分析函数的结果返回没有 IC50 值。上述的文章和方法我自己不是很清晰,需要后续抽空仔细看一看。
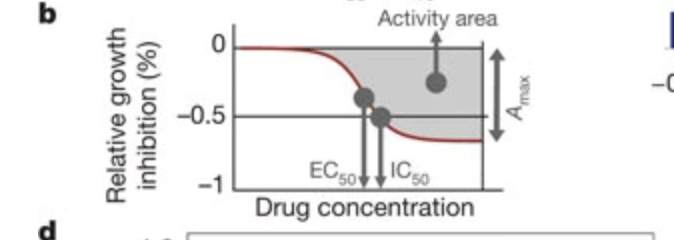
顾凯有空可以看下这个要强化的问题 目前分析和可视化的函数见 https://github.com/openbiox/UCSCXenaShiny/blob/9830b8c418a6c53aa2169b600ab81cf7347bd757/R/analyze_gene_drug_response.R#L26 https://github.com/openbiox/UCSCXenaShiny/blob/9830b8c418a6c53aa2169b600ab81cf7347bd757/R/vis_analyze_gene_drug_response.R#L10 目前可视化函数中的横坐标需要改成类似的 effect 值,目前的 mean.diff 或 median.diff 并不一定恰当,但说不准,需要做比较。也就是说,在分析函数中看能否增加得到一个类似 effect 的数据,然后和目前的做个对比。
@kaigu1990 可以运行 `vis_gene_drug_response_asso()` 并过一下使用到的代码。目前已经按haitao 提供的方式实现了,但经过交流觉得横坐标展示的指标与上面提供文献的不大符合,所以需要讨论实施怎么做到类似文献的分析图。也就是在 `analyze_gene_drug_response_asso` 获取到上面参考图中的 IC50 effect。 可以在微信里讨论。
1-2 周内彻底解决这个事。
记录一下 > copy number and mutation不过多因素可以放入到以后升级版中
@kaigu1990 你直接在下面文件的下方按照群里讨论的逻辑写一个 ` analyze_gene_drug_response_asso2` 先?后面如果觉得可以取代就将其修改为 ` analyze_gene_drug_response_asso`。建议重新拉一个分支哈,有什么问题再边做边讨论下。 https://github.com/openbiox/UCSCXenaShiny/blob/f96108bab8f8960ae6af0dc236e0167ce74e7e96/R/analyze_gene_drug_response.R#L26
另一篇主要的参考文献 [nature11005.pdf](https://github.com/openbiox/UCSCXenaShiny/files/6466641/nature11005.pdf) R语言中的药物反应分析 [pone.0146021.pdf](https://github.com/openbiox/UCSCXenaShiny/files/6466646/pone.0146021.pdf) 示例: [S1_File.pdf](https://github.com/openbiox/UCSCXenaShiny/files/6466647/S1_File.pdf) 对应的 R 包地址:https://cran.r-project.org/web/packages/drc/index.html